叶绿素是植物光合作用吸收和传递光能的最主要色素,叶绿素的生物合成途径由一系列酶促反应完成。镁螯合酶催化原卟啉与镁离子结合,生成镁原卟啉,这是叶绿素分支途径的第一步反应,是一步耗能反应。镁螯合酶由三个亚基组成:含有活性中心的催化亚基ChlH和两个AAA家族的亚基——ChlI和ChlD。ChlI具有ATP酶活性、提供反应所需的能量,并与ChlD形成双层六聚体结构。催化亚基ChlH的主要状态是单体,分子量约为150 kDa。电镜结构显示,ChlH的结构是一个不规则的笼状,然而由于分辨率不高,其活性中心的结构信息仍然缺乏。
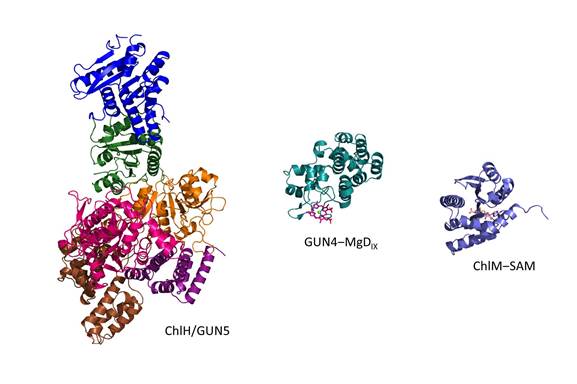
中国科学院植物研究所刘琳研究组与中国科学技术大学龚为民研究组合作,解析了光合蓝细菌集胞藻ChlH的2.5 Å分辨率结构,发现它可以分为6个结构域,形似一个沙槌。蛋白N端的两个结构域构成槌柄,其余4个结构域构成一个大致球形的槌头。在第3和第5个结构域之间,包含了一个能够容纳原卟啉的空腔。研究人员通过对各类光合生物的ChlH氨基酸序列进行比对,发现构成这一空腔的氨基酸非常保守,推测它就是镁螯合酶的活性中心。位于第3个与第5个结构域之间的一个丙氨酸的缬氨酸突变体对应于拟南芥的“基因组解偶联”表型5(genomes uncoupled 5, GUN5)的突变,因此ChlH也被称作GUN5。研究人员推测该突变造成第3个与第5个结构域之间的阻碍,导致酶的活性降低。集胞藻ChlH/GUN5的结构是第一个高分辨率的镁螯合酶催化亚基结构,为深入研究这样一个复杂的酶的催化机理打下了基础。该进展发表于2015年第9期的《自然-植物》(Nature Plants)。
镁螯合酶的底物原卟啉和产物镁原卟啉均可被GUN4蛋白结合。已有的GUN4结构由于没有结合卟啉,不能确切地描述卟啉的结合方式。刘琳研究组获得了集胞藻GUN4结合次卟啉(原卟啉的类似物)的1.5 Å分辨率结构以及结合镁次卟啉的2.0 Å结构,发现GUN4以一种半开放型的方式结合卟啉,有利于卟啉分子的传递。该进展作为封面文章发表于2015年第7期的《分子植物》(Molecular Plant)。研究组另一项工作发现,镁原卟啉上第13位丙酸侧链的羧基甲基化由镁原卟啉甲基转移酶ChlM(叶绿素分支途径的第二个酶)催化,研究得到的集胞藻ChlM与甲基供体SAM的复合物结构揭示了参与催化的关键氨基酸残基。该进展发表于2014年第37期的《生物化学杂志》(The Journal of Biological Chemistry)。
刘琳研究组博士生陈学敏(已毕业)是这三篇文章的第一作者。研究得到了科技部973计划(2011CBA00901)、国家自然科学基金(31340044)、中科院重大突破择优支持(KGZD-EW-T05)和中科院“百人计划”的资助。